昨天我们介绍了一些网络分析当中用到的一些基础的知识(相互作用网络分析基础 )。对于基因组数据分析而言的话,我们能用到网络分析的就是蛋白相互作用分析(protein-protein ineraction, PPI)分析了。
蛋白相互作用分析的数据库有很多,至于为什么选择STRING,还是在于其强大的可视化,以及自定义功能。这样我们可以得到数据结果的同时,还可以得到相对好看的图。下面我们就来介绍一下STRING数据库如何使用吧~
基本检索
我们在打开数据库之后,在菜单栏可以看到很多种来进行相互作用关系预测的选项。如果我们有一个目标蛋白,想要查看这个蛋白的可能的相互作用蛋白可以选择 Protein by name;如果我们有很多蛋白,想要查看这些蛋白之间的相互作用关系,那就可以选择 Multiple proteins。
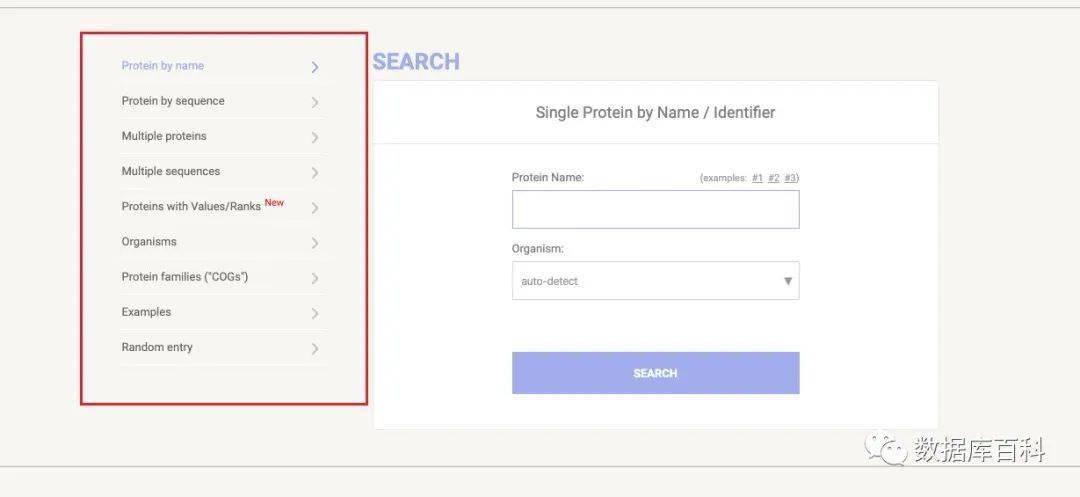
由于我们在之前的差异表达分析的时候,可以得到很多基因,所以我们这里选择 Multiple proteins来进行下一步分析。这里我们需要的输入的就是基因名即可,基因名与基因名之间通过通过换行来间隔。另外需要做的就是选择目标物种,由于我们做的是人的分析,所以选择人即可。
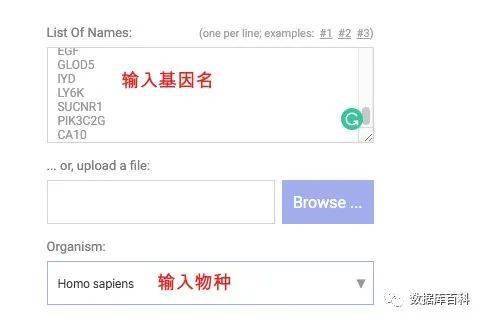
接下来点击 SEARCH即可。这个时候需要注意的是,点击完之后,页面会马上弹出来。但是对于目标蛋白是不是全部都输入全了。我们需要一直往下拉页面,在最下面看到 continue这个按钮。点击最下面这个才算是加载完了。
我们点击完之后,就可以看到直接分析的结果了。
结果介绍
首先我们看到的分析结果是就是一个相互作用网络的图。对于这个网络,我们可以通过鼠标来拖动每个node。来使得图形更好看一些。这样也可以导出来直接用了。

下面就是关于这个网络的这种设定以及自定义了。
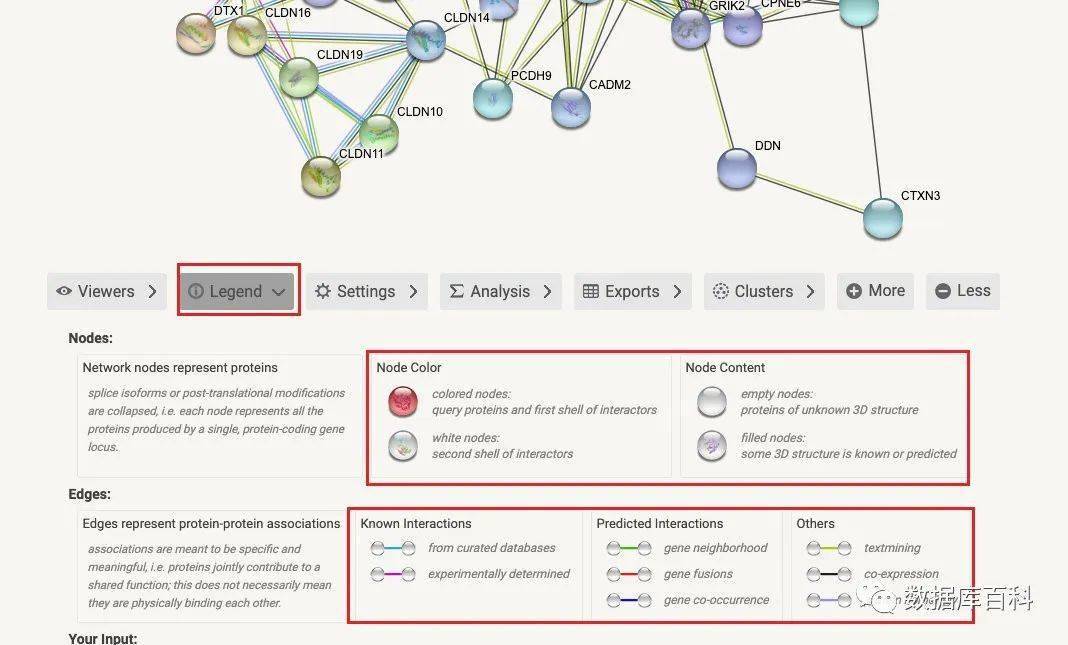
图例(legend)
首先我们可以看到对于结果的注释,里面标注了不同的node和不同的edges代表什么。(如果不知道node和edge是什么,建议看一下昨天的帖子哦。)
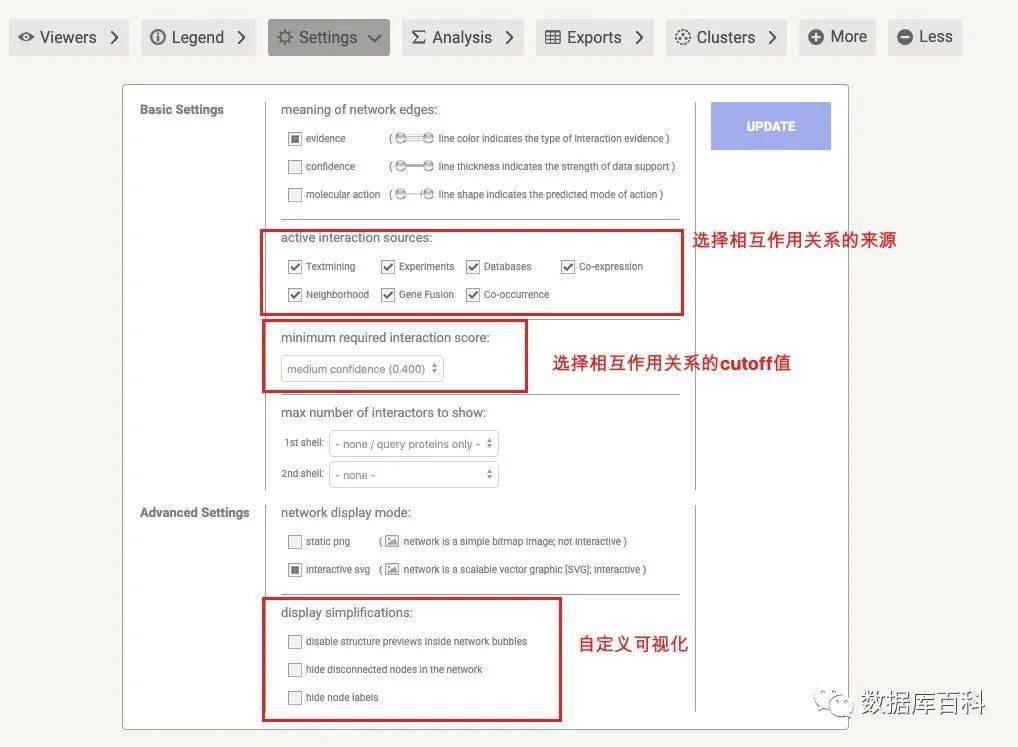
设定(setting)
在设定里面,我们可以设置自定义来设定不同的结果。我们可以选择不同的数据来源,可以设定相互作用的界限以及设定网络图的设置。
分析(Analysis)
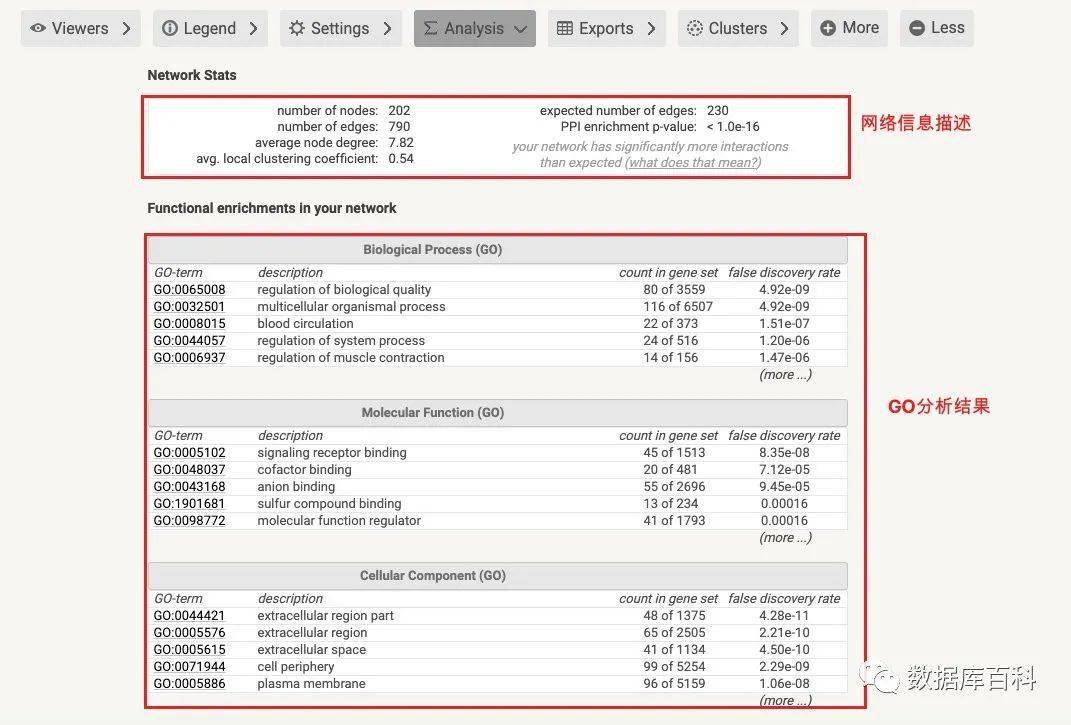
对于输入的基因,这个数据库也是可以进行GO和KEGG分析的。另外呢,由于是网络分析,所以对于网络的基本信息也是有简单的描述的。
导出(Exports)
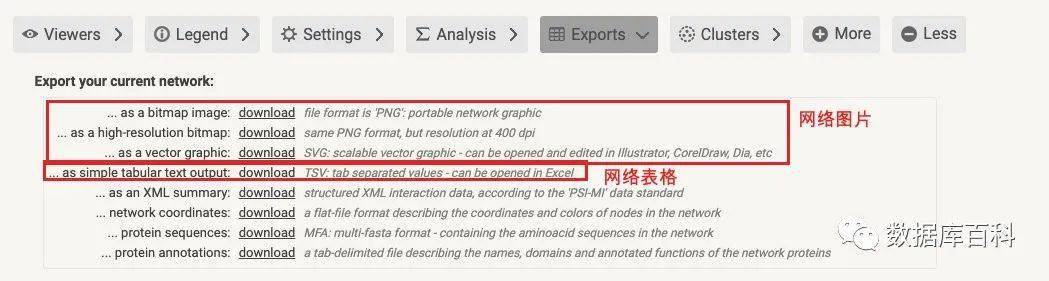
对于网络的结果,我们可以在导出当中导出相关的结果。其中就包括,一开始看到的网络图,以及包含网络edge信息的数据结果。
写在最后:
基本上对于STRING的蛋白相互作用分析就是这么多。这个只是通过数据库确定基因之间的相互作用关系,但对于寻找核心基因,还没进行查找。明天我们来介绍一下如何进行核心基因的查找。- 本文固定链接: https://maimengkong.com/kyjc/1051.html
- 转载请注明: : 萌小白 2022年6月28日 于 卖萌控的博客 发表
- 百度已收录
